Si le patient existe déjà :
Sélectionnez-le dans la liste déroulante
S'il s'agit d'un nouveau patient :
Sélectionnez "Nouveau Patient" dans le menu "Patient".
Remplissez les champs de la feuille de renseignement.
Acquisition d'une image avec différents filtres
Amélioration des signaux fluorescents acquis
Suppression d'un plan à l'écran
→ Lors du démarrage de Lucky, choisissez le mode : Caryotype.
Si le patient existe déjà :
Sélectionnez-le dans la liste déroulante
S'il s'agit d'un nouveau patient :
Sélectionnez "Nouveau Patient" dans le menu "Patient".
Remplissez les champs de la feuille de renseignement.
Si la lame existe déjà :
S'il s'agit d'une nouvelle lame :
Sélectionnez "Nouvelle Lame" dans le menu "Lame".
Remplissez les champs de la feuille de renseignement.
Cliquez
sur l'icône "Vidéo temps réel"
:
![]()
Faites en sorte que tous les chromosomes apparaissent à l'écran.
Faites la mise au point.
Réglez au mieux les paramètres d'acquisitions proposés dans la fenêtre.
Cliquez sur "Capturer dans un nouveau cas" pour acquérir l'image.
Lorsque le sablier disparaît, l'image est acquise. Cliquez sur "Fermer" et retournez dans la fenêtre Mitose.
Cliquez sur l'icône
"Enregistrer"
![]() et remplissez les coordonnées de la mitose dans la
fenêtre "Info Mitose" qui apparaît
alors. Cliquez sur OK. Une fenêtre "Nouveau Cas"
apparaît. Cliquez sur OK pour confirmer. Si c'est la
première fois que le cas est enregistré, un nouveau
numéro lui est attribué (correspondant au nombre de
mitoses prises sur cette lame) et celui-ci est affiché dans
le champ de sélection des métaphases
et remplissez les coordonnées de la mitose dans la
fenêtre "Info Mitose" qui apparaît
alors. Cliquez sur OK. Une fenêtre "Nouveau Cas"
apparaît. Cliquez sur OK pour confirmer. Si c'est la
première fois que le cas est enregistré, un nouveau
numéro lui est attribué (correspondant au nombre de
mitoses prises sur cette lame) et celui-ci est affiché dans
le champ de sélection des métaphases
![]()
Si tous les chromosomes ne tiennent pas à l'écran, il faut acquérir plusieurs images de la métaphase.
Vous disposez selon le nombre de chromosomes manquants ou selon vos préférences de plusieurs possibilités :
Il ne manque que quelques chromosomes et vous les importez par copier-coller (la nouvelle métaphase ainsi créée ne correspondra plus exactement à la réalité)
Prenez une première métaphase avec le maximum de chromosomes.
Changez le champs du microscope et
capturez la nouvelle image en cliquant sur le bouton "Ajouter
au cas courant". Quittez la fenêtre Vidéo
et enregistrez éventuellement le cas. Le nouveau cas est
alors constitué de deux images. Vous pouvez passer de l'une
à l'autre grâce à la nouvelle liste déroulante
![]() apparue à droite de la liste des cas. Extrayez le ou
les chromosomes manquants avec le bouton droit de la souris
"Extraire ici", la flèche de la souris
étant dessus. Copiez ensuite ce chromosome extrait en
cliquant sur "Copier cette extraction" avec le
bouton droit, la flèche étant sur le chromosome.
Revenez sur la première métaphase, en cliquant dessus
dans la fenêtre Mitose. Importez les chromosomes qui
ont été copiés en cliquant sur "Coller
cette extraction" avec le bouton droit. Les chromosomes
"collés" vont se placer dans la première
métaphase mais à la place correspondant à
celle qu'ils avaient dans leur métaphase d'origine. Leur
contour est jaune. S'ils sont à un endroit gênant,
déplacez-les avec la souris et incrustez-les en cliquant sur
"Incruster cette importation" avec le bouton droit
de la souris (si vous avez changé d'avis, cliquez sur
"Supprimer cette extraction"). Une fois le
chromosome incrusté, son contour change de couleur et
l'incrustation est irréversible. Enregistrez la métaphase
et supprimez le contour des chromosomes collés en cliquant
sur l'icône
apparue à droite de la liste des cas. Extrayez le ou
les chromosomes manquants avec le bouton droit de la souris
"Extraire ici", la flèche de la souris
étant dessus. Copiez ensuite ce chromosome extrait en
cliquant sur "Copier cette extraction" avec le
bouton droit, la flèche étant sur le chromosome.
Revenez sur la première métaphase, en cliquant dessus
dans la fenêtre Mitose. Importez les chromosomes qui
ont été copiés en cliquant sur "Coller
cette extraction" avec le bouton droit. Les chromosomes
"collés" vont se placer dans la première
métaphase mais à la place correspondant à
celle qu'ils avaient dans leur métaphase d'origine. Leur
contour est jaune. S'ils sont à un endroit gênant,
déplacez-les avec la souris et incrustez-les en cliquant sur
"Incruster cette importation" avec le bouton droit
de la souris (si vous avez changé d'avis, cliquez sur
"Supprimer cette extraction"). Une fois le
chromosome incrusté, son contour change de couleur et
l'incrustation est irréversible. Enregistrez la métaphase
et supprimez le contour des chromosomes collés en cliquant
sur l'icône
![]() . Pour sélectionner plusieurs chromosomes à
copier et coller, utilisez la touche CTRL.
. Pour sélectionner plusieurs chromosomes à
copier et coller, utilisez la touche CTRL.
Vous avez trop de chromosomes pour les prendre à partir de 2 métaphases. Vous prenez plusieurs métaphases puis faites une fusion de ces images pour avoir tous vos chromosomes sur une même métaphase.
Ouvrez la fenêtre Options en cliquant sur l'onglet "extraction" de la rubrique "Options" du menu "Fenêtres" (ou appuyez sur F3).
Placez la barre de seuil bleue, en cliquant dessus, au pied du pic le plus pointu.
Réglez les paramètres d'acquisition :
Contraste : en déplaçant vers le haut ou le bas les 2 carrés intermédiaires.
Noir : en déplaçant vers la gauche ou la droite le carré du bas (ou en déplaçant les curseurs correspondants).
Blanc : en déplaçant vers la gauche ou la droite le carré du haut (ou en déplaçant les curseurs correspondants)
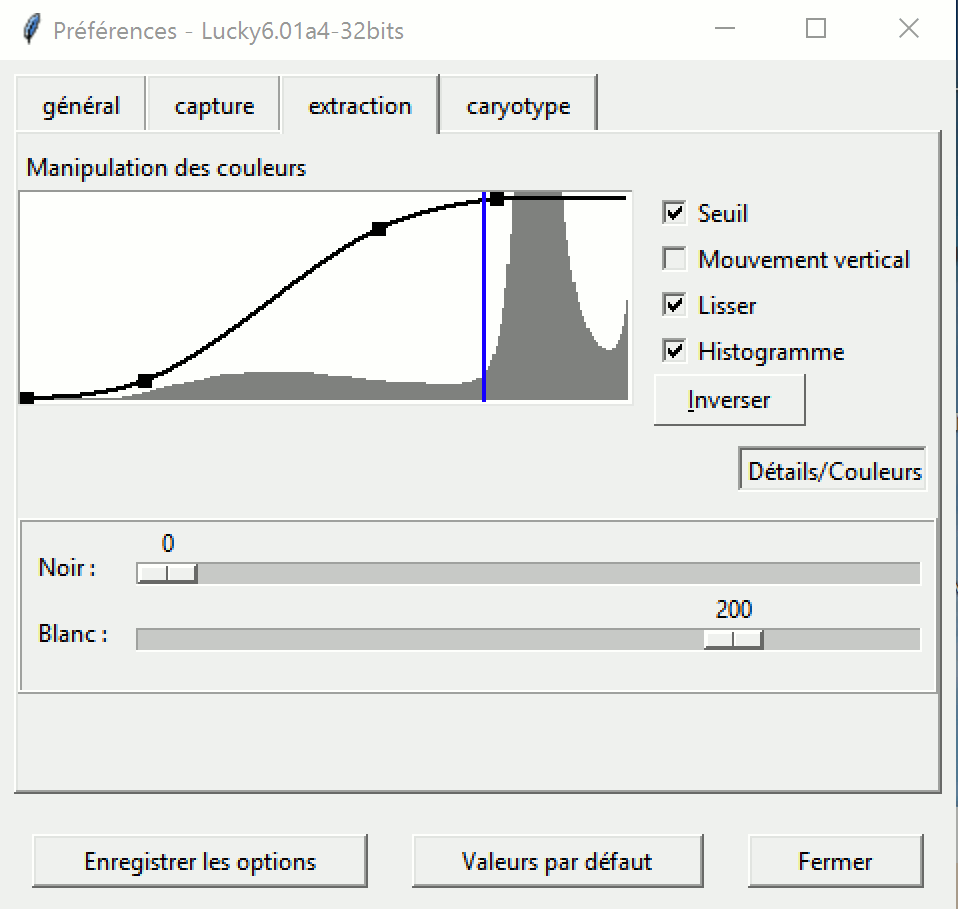
Cliquez éventuellement sur "Fermer" (ou sur la croix en haut à droite) pour fermer la fenêtre "Options".
Sélectionnez le patient (Sélection d'un patient)
Sélectionnez la lame sur laquelle se trouve la mitose (Sélection d'une lame)
Sélectionnez la mitose:
sélectionnez "Extraction automatique" dans le menu "Commandes"
ou faites un clic droit et sélectionnez "Tout extraire"
ou appuyez sur CTRL-X
Les
chromosomes extraits par le logiciel sont entourés d'un trait
de couleur différente pour deux chromosomes voisins. Le nombre
de chromosomes individualisé est indiqué dans le coin
inférieur gauche de la fenêtre (N :)
S'il n'y en a qu'une, placez la souris dessus et sélectionnez la rubrique "Supprimer cette extraction" du menu contextuel (bouton droit de la souris) ou appuyez sur la touche Suppr.
S'il y en a plusieurs, maintenez la touche CTRL enfoncée et cliquez sur les "non chromosomes" pour les sélectionner (bouton gauche de la souris). Relâchez ensuite la touche CTRL et supprimez ces éléments en sélectionnant la rubrique "Supprimer les sélections" du menu contextuel (bouton droit de la souris). Pour aller plus vite, vous pouvez appuyer sur la touche Suppr à chaque fois que vous sélectionnez une extraction.
Placez la souris sur un des 2 chromosomes et sélectionnez la rubrique "Séparation automatique" du menu contextuel (bouton droit de la souris) ou appuyez sur la barre d'espace (raccourci clavier). Une fois que les chromosomes sont séparés, le contour de chaque chromosome est d'une couleur différente.
Si la séparation automatique n'est pas faite correctement :
placez la souris dessus et sélectionnez la rubrique "Supprimer cette extraction" du menu contextuel (bouton droit de la souris), puis sélectionnez "Extraire ici" dans le même menu contextuel.
faites une séparation "manuelle" (voir ci-dessous).
Une fois que les chromosomes sont séparés, leurs contours ont une couleur différente.
Tracez une ligne entre les chromosomes faussement regroupés à l'aide de la souris en maintenant le bouton gauche appuyé (commencez toujours à l'extérieur d'un chromosome).
Replacez la souris sur l'amas et séparez les chromosomes au moyen de la rubrique "Séparation" du menu contextuel (bouton droit de la souris) ou avec la barre d'espace (raccourci clavier).
Si un chromosome est découpé en plusieurs fragments, cliquez sur ceux-ci avec le bouton de gauche de la souris en maintenant la touche CTRL du clavier enfoncée, puis regroupez-les en sélectionnant "Grouper les sélections" dans le menu contextuel (bouton droit de la souris), la flèche de la souris étant sur l'un de ces chromosomes ou avec la barre d'espace (raccourci clavier).
Pour supprimer une "tache" incluse dans le contour d'un chromosome :
Appuyez sur le bouton central de la souris.
Repoussez avec la gomme symbolisée par un rond le contour du chromosome afin d'en exclure ce qui ne lui appartient pas.
Pour agrandir le contour d'un chromosome si une partie n'a pas été extraite :
Placez la flèche de la souris à l'intérieur du contour à modifier.
Appuyez sur le bouton central de la souris.
Repoussez avec la gomme symbolisée par un rond le contour du chromosome afin d'inclure ce qui lui manque.
Pour agrandir globalement le contour d'un chromosome, utilisez “Agrandir cette extraction” dans le menu contextuel. Vous pouvez aussi positionner la souris sur l’extraction et appuyer sur la touche <Up> du clavier ou appuyer sur la touche <Shift> et tourner la molette de la souris
Pour réduire globalement le contour d'un chromosome, utilisez “Réduire cette extraction” dans le menu contextuel. Vous pouvez aussi positionner la souris sur l’extraction et appuyer sur la touche <Down> du clavier ou appuyer sur la touche <Shift> et tourner la molette de la souris
Afin de séparer plus précisément les chromosomes, on peut zoomer :
Cliquez
sur le chromosome qui vous intéresse, puis choisissez "zoomer
cette extraction" dans le menu contextuel (bouton droit de
la souris), ou double-cliquez sur le chromosome à agrandir,
ou appuyez sur la touche z.
Pour revenir à la taille
initiale, cliquez en dehors d'un chromosome avec le bouton droit de
la souris et sélectionnez "taille normale"
ou double cliquez en dehors d'un chromosome ou encore appuyez sur la
touche z (raccourci clavier).
Maintenir la touche Ctrl appuyée puis tournez la molette de la souris.
Faites un clic droit dans la zone "Facteur d'échelle" en haut à droite de la fenêtre et sélectionnez une valeur. Pour revenir à la taille initiale, faites un clic droit et sélectionnez "100" dans le menu contextuel.
Placez la souris sur le chromosome à extraire et sélectionnez "Extraire ici" dans le menu contextuel (bouton droit de la souris).
Le logiciel propose différentes fonctions à l'utilisateur pour vérifier le nombre de chromosomes extraits :
Le nombre
de chromosomes extraits affiché en bas à gauche de la
fenêtre :
![]()
Une fonction de comptage (sélectionnez "Comptage" dans le menu "Commandes").
Les
chromosomes extraits peuvent être visualisés colorés
pleinement en les sélectionant tous grâce à
l'icône
![]() ; ce qui permet de mieux repérer
les fausses extractions ou les chromosomes regroupés.
; ce qui permet de mieux repérer
les fausses extractions ou les chromosomes regroupés.
Sélectionnez "Classification automatique", dans le menu "Commandes"
Ou sélectionnez "Classification automatique" dans le menu contextuel (clic sur le bouton droit de la souris)
Ou appuyez sur les touches CTRL-W
Les chromosomes mal classés peuvent être déplacés à l'aide de la souris.
Les centromères peuvent être ajustés sur la ligne en les déplaçant avec la souris.
Les chromosomes peuvent être tournés d’un demi-tour par un double-clic de souris ou via "Retourner" du menu contextuel. Il est aussi possible d’appliquer un effet miroir grâce à "Miroir horizontal" du menu contextuel.
L'orientation fine des chromosomes peut être corrigée :
Soit grâce à la molette de la souris
Soit en maintenant la touche Ctrl enfoncée puis à l’aide du bouton gauche de la souris en tirant un trait à partir du centromère vers l'extérieur du chromosome et en l’orientant sur 360° .
Les "non chromosomes" peuvent être supprimés grâce à la rubrique "Supprimer la sélection" du menu contextuel (clic droit sur le faux chromosome).
Si un chromosome n'a pas été extrait, extrayez-le dans la fenêtre Mitose en laissant la flèche dessus et en cliquant sur "Extraire Sélection" dans le menu contextuel (bouton droit) puis amenez-le à sa place dans le caryotype.
Si un mauvais découpage a été réalisé lors de l'extraction, vous pouvez le modifier dans la fenêtre Mitose, puis faire glisser les chromosomes bien séparés dans la fenêtre Caryotype.
Si l'ensemble des chromosomes d'une métaphase n'a pas pu être acquis en une seule image (y compris avec le copier-coller) :
Acquérir deux métaphases en ajoutant la deuxième au cas courant
Extraire et caryotyper la première métaphase
L'enregistrer
en cliquant sur l'icône
![]() .
.
Afficher
la deuxième métaphase en la sélectionnant dans
la liste déroulante
![]()
Extraire et caryotyper la deuxième métaphase dont les chromosomes vont venir se classer sur le caryotype déjà commencé.
Faire d'éventuelles corrections manuelles
Lors de la visualisation des chromosomes du caryotype sur la métaphase, c'est la métaphase contenant le chromosome choisi qui s'affiche automatiquement dans la fenêtre Mitose.
Dans la fenêtre Caryotype :
Placez le curseur sur le chromosome que vous voulez repérer dans la métaphase.
Ce chromosome apparaîtra alors entouré de rouge sur la métaphase et le chromosome qui lui est apparié sera en bleu.
Dans la fenêtre Mitose :
Placez le curseur sur le chromosome que vous voulez repérer dans le caryotype. Ce chromosome aura alors un contour rouge et celui qui lui est apparié un contour bleu.
Ce chromosome apparaîtra alors entouré d'un rectangle rouge dans le caryotype et celui qui lui est apparié aura un rectangle bleu. Il ne faut pas que les rectangles recouvrent une partie du chromosome homologue, car cette partie ne sera pas imprimée.
Si tous les chromosomes ont des contours trop ajustés ou trop éloignés :
Placez le curseur dans la fenêtre Caryotype en dehors d'un chromosome.
Sélectionnez "Agrandir toutes les extractions" ou "Réduire toutes les extractions" dans le menu contextuel (bouton droit de la souris) pour respectivement agrandir ou diminuer le contour des chromosomes, ou appuyez sur les flèches haut ou bas (raccourcis clavier)
Répétez l'opération jusqu'à l'obtention de la taille souhaitée.
Si vous voulez modifier globalement le contour d'un chromosome :
Placez le curseur sur ce chromosome.
Sélectionnez "Agrandir cette extraction" ou "Réduire cette extraction" dans le menu contextuel (bouton droit de la souris) pour respectivement agrandir ou diminuer le contour du chromosome ou appuyez sur les flèches haut ou bas (raccourcis clavier).
Répétez l'opération jusqu'à l'obtention de la taille souhaitée.
Les débords chromosomiques liés aux croisements peuvent être supprimés en gommant ces derniers sur la fenêtre Mitose :
Placez-vous dans la fenêtre Mitose, au niveau à modifier.
Appuyez sur le bouton central de la souris : un rond apparaît.
En poussant ce rond, vous déplacez le contour chromosomique à modifier (c'est le premier contour touché qui est modifié et le rond prend alors la couleur de ce contour).
Vous pouvez modifier la taille du rond avec les touches + ou -
Pour travailler avec plus de précisions, vous pouvez au préalable zoomer sur le chromosome dont vous voulez modifier le contour.
Un commentaire peut être ajouté dans le bas de la fenêtre Caryotype :
Sélectionnez "Informations..." dans le menu "Cas".
Ecrivez dans la fenêtre (la souris étant à l'intérieur) la formule chromosomique, ainsi qu'un éventuel commentaire. Les dernières formules utilisées figurent dans un menu accessible par un clic droit.
Les renseignements sur le patient ainsi que les coordonnées de la métaphase (données des fiches de renseignements "patient" et "lame") apparaîtront de façon systématique.
Un ou plusieurs chromosomes peuvent être fléchés et annotés aussi bien dans la fenêtre Mitose que dans la fenêtre Caryotype.
Cliquez sur le bouton droit là où vous souhaitez insérer le commentaire et sélectionnez "Annotation" dans le menu contextuel.
Sélectionnez "Flèche" ou "Texte".
Vous pouvez également
utiliser l’outil «flèche» dans la barre
d’outil :
![]() pour créer une flèche en
cliquant simplement à l’endroit désiré
ou l’outil «texte»
pour créer une flèche en
cliquant simplement à l’endroit désiré
ou l’outil «texte»
![]() pour créer de la même
façon un texte. Revenez ensuite au mode de sélection
normal en cliquant sur l'outil de sélection
pour créer de la même
façon un texte. Revenez ensuite au mode de sélection
normal en cliquant sur l'outil de sélection
![]() .
.
Si vous souhaitez agrandir tous les chromosomes du caryotype, cliquez dans la fenêtre facteur d'échelle et tapez au clavier la valeur souhaitée, puis appuyez sur Entrée.
Pour enregistrer la métaphase caryotypée ou pas
La mitose correspondant alors au caryotype apparaîtra soulignée dans le menu déroulant des mitoses.
Sélectionnez "Options" dans le menu "Fenêtres". La fenêtre Options s'affiche. Sélectionnez l'onglet "général" pour définir les paramètres d'impression :
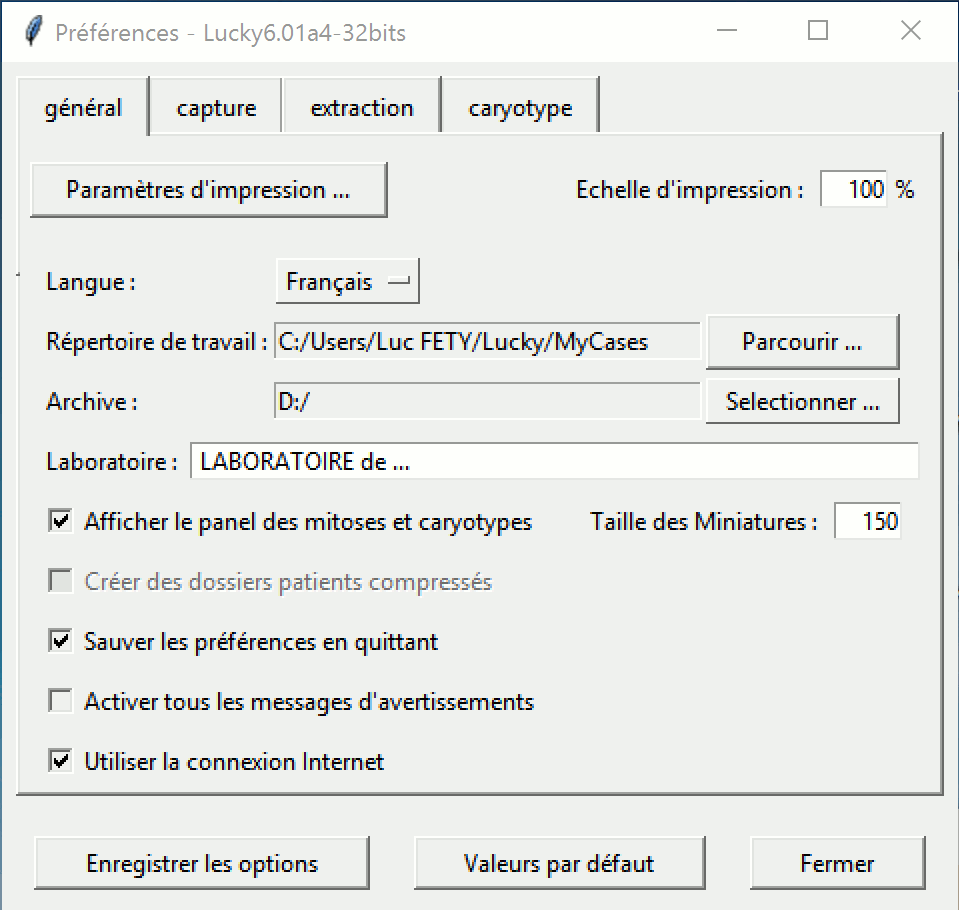
Cliquez sur "Paramètres d'impression…" pour sélectionner et configurer votre imprimante.
Sélectionnez
l'échelle d'impression en cliquant sur

Cliquez
sur l'icône
![]() de la fenêtre à imprimer (Mitose ou Caryotype).
Vous pouvez aussi sélectionner "Imprimer…"
dans le menu Fichier.
de la fenêtre à imprimer (Mitose ou Caryotype).
Vous pouvez aussi sélectionner "Imprimer…"
dans le menu Fichier.
Sélectionnez "Fermer le cas" dans le menu "Fichier".
→ Lors du démarrage de Lucky, choisissez le mode Fish.
Si le patient existe déjà, sélectionnez-le dans le menu déroulant "Patient".
Si ce n'est pas le cas, sélectionnez "Nouveau patient" dans le menu "Patient" et remplissez les rubriques d'informations sur le patient.
Si la lame existe déjà, sélectionnez-la dans le menu déroulant "Lame".
Si ce n'est pas le cas, sélectionnez "Nouvelle lame" dans le menu "Lame"et remplissez les rubriques d'informations sur la lame.
Prenez la première image, par exemple avec le filtre DAPI
Cliquez
sur l'icône "Vidéo Temps Réel"
![]() .
.
Vérifiez que vous avez bien tous les chromosomes à l'écran, sinon ajustez le champ et tournez au besoin la caméra.
Faites la mise au point et réglez les paramètres d'acquisition en bougeant les curseurs dans les onglets noir et blanc pour jouer respectivement sur le contraste et la brillance.
Choisissez le filtre bleu dans le menu déroulant "Filtre".
Réglez le paramètre d'intégration sur 2.
Cliquez sur "Capturer le cas courant".
L'image est prise quand la flèche de la souris réapparaît à la place du sablier.
Prenez alors la deuxième image avec le filtre correspondant au fluorochrome d'intérêt.
Réglez les paramètres d'acquisition en bougeant les curseurs dans les onglets noir et blanc pour jouer respectivement sur le contraste et la brillance. Faites en sorte que le signal fluorescent soit le plus brillant possible et le fond le plus sombre.
Choisissez le filtre adéquat rouge ou vert dans le menu déroulant "Filtre".
Réglez le paramètre d'intégration entre 16 et 256 selon l'intensité du signal fluorescent.
Cliquez sur "Ajouter au cas courant".
L'image est prise quand la flèche de la souris réapparaît à la place du sablier.
S'il y a 2 fluorochromes, prenez la troisième image avec le filtre adéquat.
Lorsque toutes les images ont été prises avec les filtres adéquats, cliquez sur "Fermer".
Les différentes images prises avec les filtres successifs vont être superposées les unes sur les autres et l'image avec les différents plans va apparaître à l'écran.
Cliquez sur "Options" dans le menu "Fenêtres" (ou appuyez sur F3).
A chaque image prise avec les différents filtres correspond une fenêtre de réglage rouge, verte et bleue.
Dans chaque fenêtre, est représentée la courbe du signal fluorescent.
Pour augmenter l'intensité du signal fluorescent, déplacez horizontalement le curseur du haut, pour l'amener juste à droite de la pointe de la courbe.
Pour diminuer le bruit de fond, déplacez horizontalement le curseur du bas, pour l'amener juste à gauche du pied de la courbe.
Au fur et à mesure des "réglages" dans chaque fenêtre, vous voyez en temps réel les modifications que vous faites sur l'image avec les 3 plans superposés.
Enregistrez
l'image avec les réglages qui vous conviennent en cliquant
sur l'icône
![]() .
.
Si vous souhaitez supprimer un des plans pour mieux visualiser les 2 autres ou ne garder qu'un plan de fluorochrome sans les chromosomes en DAPI, cliquez sur le carré qui se trouve devant le ou les plan(s) à désactiver ou réactiver.
Choisissez le plan de couleur à déplacer dans la fenêtre affichant les 3 types de plan : bleu, vert, rouge en cliquant dessus.
Cliquez sur ce que vous voulez déplacer.
En maintenant le bouton de gauche de la souris enfoncé, tracez un trait dans la direction souhaitée et de la taille du déplacement voulu (trait jaune). Lorsque vous relâchez le bouton, le déplacement est effectué.
Si vous voulez modifier ce déplacement, refaites un nouveau trait, le précédent apparaissant alors en rouge. Pour annuler le déplacement, placez le trait jaune sur le rouge.
Pour
insérer une flèche, cliquez sur
![]() et amenez la flèche sur un noyau (plus visible sur
fond bleu que noir), puis déplacez la flèche en
cliquant dessus avec le bouton gauche de la souris, représenté
par une petite flèche bleue. Il est également possible
de changer l'orientation de la flèche en cliquant au bout et
en déplaçant la souris dans le sens souhaité.
On peut supprimer la flèche, modifier son épaisseur
(croissante de 1 à 5), modifier sa pointe (taille de 1 à
5) ou modifier sa couleur en cliquant sur l'une de ces propositions
dans le menu contextuel obtenu avec le bouton droit de la souris.
Pour modifier la couleur, déplacez les curseurs du rouge, du
vert ou du bleu jusqu'à l'obtention de la couleur souhaitée
qui apparaît dans le carré, puis cliquez sur ok.
et amenez la flèche sur un noyau (plus visible sur
fond bleu que noir), puis déplacez la flèche en
cliquant dessus avec le bouton gauche de la souris, représenté
par une petite flèche bleue. Il est également possible
de changer l'orientation de la flèche en cliquant au bout et
en déplaçant la souris dans le sens souhaité.
On peut supprimer la flèche, modifier son épaisseur
(croissante de 1 à 5), modifier sa pointe (taille de 1 à
5) ou modifier sa couleur en cliquant sur l'une de ces propositions
dans le menu contextuel obtenu avec le bouton droit de la souris.
Pour modifier la couleur, déplacez les curseurs du rouge, du
vert ou du bleu jusqu'à l'obtention de la couleur souhaitée
qui apparaît dans le carré, puis cliquez sur ok.
Pour
insérer un texte, cliquez sur
![]() et amenez la lettre sur un noyau (plus visible sur fond bleu
que noir), puis déplacez le curseur en cliquant dessus avec
le bouton gauche de la souris et amenez-le là où vous
souhaitez insérer un commentaire. Vous pouvez modifier la
police en sélectionnant Police dans le menu
contextuel.
et amenez la lettre sur un noyau (plus visible sur fond bleu
que noir), puis déplacez le curseur en cliquant dessus avec
le bouton gauche de la souris et amenez-le là où vous
souhaitez insérer un commentaire. Vous pouvez modifier la
police en sélectionnant Police dans le menu
contextuel.
Une
fois les annotations faites, cliquez sur l’outil
![]() pour revenir en mode sélection.
pour revenir en mode sélection.
Allez dans l'onglet "général" de la fenêtre "Options" et choisissez votre imprimante dans la liste déroulante.
Pour archiver un dossier de patient :
Régler correctement le chemin de l’unité d’archivage dans le champ "Archive" de la fenêtre des "Préférences" onglet "Général".
Cochez le ou les patients à archiver dans la liste déroulante "Patient".
Sélectionnez "Archiver le patient sélectionné" dans le menu contextuel ou dans le menu "Patient".
Indiquer si nécessaire un nom pour l’unité d’archivage. Ce nom permet d’entretenir la base de données de cas archivés de manière à retrouver facilement ces derniers.
L’archivage s’effectue.
Un message indique que l'archivage est terminé et demande si l'on veut supprimer ce dossier du disque dur.
Supprimez les dossiers archivés du disque en cliquant sur Supprimer et confirmez en cliquant sur Oui.
Pour voir la liste des dossiers archivés dans l’unité d’archivage :
Pour imprimer la liste des patients archivés sur un zip :
Sélectionnez "Imprimer la liste des patients" dans le menu "Patient".
Réglez éventuellement l'échelle d'impression en sélectionnant "Option" dans le menu "Fenêtres" (ou F3), puis en cliquant sur l'onglet "Général".
Pour visualiser un caryotype ou une mitose d'un patient déjà archivé :
Cliquez
sur l'icône symbolisant le répertoire de travail
![]() pour faire apparaître l’icone symbolisant l’unité
d’archivage
pour faire apparaître l’icone symbolisant l’unité
d’archivage
![]() .
.
Sélectionnez ensuite simplement dans les listes déroulantes le patient, la lame et la mitose de la même manière que s’il s’agissait du répertoire de travail. Remarque : par soucis de sécurité, les cas archivés ne peuvent pas être modifiés. Mais il est possible en cas de besoin de les restaurer pour éventuellement apporter une modification.
Pour restaurer un cas archivé :
Si vous
ne connaissez pas le chemin de l’unité d’archivage,
faites apparaître
l’Icône "Base
de Données"
![]() à la place de l’icône "Répertoire de
travail"
à la place de l’icône "Répertoire de
travail"
![]() puis sélectionnez le patient, la lame et le cas à
recherché. Il vous sera alors indiqué où le
patient à été archivé.
puis sélectionnez le patient, la lame et le cas à
recherché. Il vous sera alors indiqué où le
patient à été archivé.
Faire
apparaître l’icône "Unité
d’archivage"
![]() à la place de l'icône "Répertoire
de travail"
à la place de l'icône "Répertoire
de travail"
![]() .
.
Sélectionnez ensuite simplement dans la liste déroulante "Patient" le patient à restaurer.
Sélectionnez "Restaurer le patient sélectionné" dans le menu contextuel (clic droit) ou dans le menu "Patient".
Sauvegarger éventuellement les cas ouverts.
Sélectionnez "Quitter" dans le menu "Fichier" pour quitter l’application.